Сбор дифракционных данных комплекса S15-16SрРНК (S15 T3C мутант) проводился на синхротроне ESRF (Гренобль, Франция), линия ID14 С использованием детектора Mar CCD (l= 0.93300 Å; Т=100К).
Полученные данные обрабатывали программами DENZO и SCALEPACK. Обработка данных имеет ряд этапов:
Выделение сильных рефлексов;
Предсказание обратной решётки;
Определение пространственной группы и параметров ячейки;
Уточнение параметров кристалла и детектора;
Обработка всех имеющихся изображений;
Приведение рефлексов к общей шкале;
Интегрирование рефлексов по всему обратному пространству.
В результате мы получили набор дифракционных данных в обратном пространстве.
Решение проблемы фаз
Первоначальный набор фаз получен с помощью метода молекулярного замещения. Основой для модели послужила структура с заменой Met на SeMet комплекса S15(I11M+A79M)-16SрРНК.
Для решения задачи молекулярного замещения использовалась процедура оптимизации ориентации и положения модели как твердого тела по методу сопряженных градиентов. Расчеты проводились с помощью программы комплекса CNS RIGIT-BODY REFINEMENT. Полученный R-фактор (0,339), показал, что при общей гомологии комплексов (»99%) всё же наблюдается расхождение в боковых цепях и петлях.
Построение и уточнение модели
Первоначально были проведены несколько циклов автоматического (программой CNS) кристаллографического уточнения, которое включало в себя молекулярно-динамическую процедуру моделированного отжига (ANNELING), проводимую во внутренних координатах; уточняемыми параметрами были торсионные углы. При этом использовались ограничения (типа “restraints”) в соответствии с операцией некристаллографической симметрии.
Затем были получены две карты электронной плотности:
карта, рассчитанная с использованием коэффициентов 2fo-fc, где fo – структурный фактор, полученный экспериментально на основе дифракционных данных, fc – структурный фактор, рассчитанный на основе модели
composit-omit map – разностная 2fo-fc карта, где fc определяется как комбинированная величина, рассчитанная по нескольким моделям с исключением 5% атомов на каждом шаге.
Полученные карты были хорошего качества, что позволило вписать все боковые остатки белка, уточнить положение главной цепи и молекулы РНК. Для ручной правки использовалась программа молекулярной графики О.
Окончательное уточнение включало уточнение параметров длин связей и углов с помощью программы MINIMIZE (CNS), уточнение В-факторов для индивидуальных атомов, а так же проверку стереохимии полученной структуры и расстояний между атомами (водородные связи, Ван-дер-Вальсовы взаимодействия, «плохие» расстояния).
Окончательная модель, уточненная до значений R-фактора ***8% и Rfree ***% при разрешении до 2,8Е, включает ** аминокислотных остатков и ** нуклеотидов. Кроме того были локализованы *** молекул воды, ** ионов ионов Mg+2 в независимой части элементарной ячейки. Общее число атомов модели в независимой части элементарной ячейки составило ****. Модель обладает хорошими стехиометрическими параметрами и не содержит остатков, расположенных в запрещенных областях карты Рамачандрана. Часть окончательной 2Fo-Fc карты электронной плотности на уровне 1.5 s показана на рис. 20. Структура комплекса S15-16SрРНК схематически показана на рис. 21. Координаты атомов окончательной модели комплекса S15-16SрРНК занесены в RCSB Protein Data Bank (код ****).
Результаты и их обсуждение
В результате проделанной работы была построена модель структуры комплекса S15-16SрРНК (S15 T3C мутант).
Модель была уточнена до R-фактора 24,5% и Rfree 30,9% при разрешении до 2,9Е, и включает 86 аминокислотных остатков и 57 нуклеотидов. Общее число атомов модели в независимой части элементарной ячейки составило 1943. Модель обладает хорошими стехиометрическими параметрами и не содержит остатков, расположенных в запрещенных областях карты Рамачандрана.
Таблица 2.2.1. Статистика уточнения структуры комплекса комплекса S15-16SрРНК (S15 T3C мутант)
| Пространственная группа | Р6422 |
| Параметры ячейки (Е) | a=128.228, b= 128.2286, c=64.9505 |
| Длина волны (Е) | 0,933 |
| Разрешение (Е) | 500 - 2,9 |
| Избыточность | 5,9 |
| Полнота набора (%) | 98,0 |
| Rsym (%) | 3,1 |
| Rcryst/Rfree (%) | 24,5/30,9 |
| Разрешение (Е) | 6,0 – 2,9 |
| Число рефлексов | 8209 |
Вср (Е 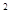 ) )
| 44,8 |
| R.m.s.d. связей (Е) | 0,006 |
| R.m.s.d. углов (°) | 1,2 |
Как видно из рисунка 2.2.1., белок S15 относится к семейству a-спиральных белков и состоит из четырёх a-спиралей, взаимодействующих с 16SрРНК и стабилизирующих данную структуру.
Фрагмент 16S рРНК из T.thermophilus (рис. 2.2.2.) длиной 57 нт состоит из укороченных спиралей Н20, Н21 и Н22. Спираль Н22 стыкуется со спиралью Н21, образуя вытянутую структуру, а спираль Н20 прилегает к ней под углом примерно в 60°.
рис.2.2.1. Структура белка S15 (T3C мутант)
рис. 2.2.2. Структура фрагмента 16S рРНК
Белок S15 распознаёт на поверхности РНК два удалённых участка, один из которых располагается в верхней части спирали H22, а другой – в районе соединения трёх спиралей РНК (рис. 2.2.3.). Участки отстают друг от друга на один виток спирали.
рис.2.2.3. Структура комплекса S15-16SрРНК (S15 T3C мутант)
Выводы:
Получен и обработан набор дифракционных данных для комплекса S15-16SрРНК (S15 T3C мутант).
Методом молекулярного замещения определена структура комплекса.
Показано, что рибосомный белок комплекса S15 связывается с 16S рРНК в двух пространственно удалённых участках.
Показано, что мутация Т3С не изменяет пространственной структуры комплекса и структуры РНК-белкового интерфейса.
Список литературы
Серганов А.А. (1997) Изучение РНК-связывающих свойств рибосомного белка S15 из Thermus thermophilus. Диссертация, МГУ.
Anston A.A., Otridge J., Brzozowski A.M., Dodson E.J., Dodson G.G., Wilson K.S., Smith T.M., Yang M., Kurecki T., Gollnick P. (1995). Biochemestry. 18: 693-700
Argos P. & Rossmann M.G. (1980) in “Theory and Practice of Direct Methods in Crystallography” (Ladd and Palmer, eds.), pp.361-417. Plenum, New York.
Bentley G.A. & Houndusse A. (1992), Acta Cryst. A48, 312-322.
Blundell T.L. & Johnson L.N. (1974) Protein Crystallography. Academic Press, New York.
Brunger A.T., Adams P.D., Clore G.M., DeLano W.L., Gros P., Grosse-Kunstleve R.W., Jiang J., Kuszewski J., Nilges M., Pannu N.S., Read R.J., Rice L.M., Simonson T., Warren G.L. (1998) Crystallography & NMR System: A New Software Suite for Macromolecular Structure Determination. Acta Cryst. D54, 909-921.
Brunger A.T., Milburn M.V., Tong L., de Vos A.M., Jancarik J., Yamazumi Z., Nishimura S., Ohtsuka E., Kim S.-H. (1990), Proc. Natl. Acad. Sci. USA 87, 4849-4853.
Burd C.G. Dreifuss G. (1994). Conserved structures and diversity of functions of RNA-binding proteins. Science 265: 615-620
Bycroft M., Grunert S., Murzin A., Proctor M., Johnston D. (1995). NMR solution structure of a dsRNA binding domain from Drosophila staufen protein reveals homology to the N-terminal domain of ribosomal protein S5. EMBO J. 14: 3563-3571
Bycroft M., Hubbard T.J.P., Proctor M., Freund S.M.V., Murzin A. (1997). The solution structure of the S1 RNA binding domain: a member of an ancient nucleic acid-binding fold. Cell 88: 235-242
Castellano E., Oliva G., Navaza J. (1992), J. Appl. Cryst. 25, 281.
Cate J.H., Gooding A.R., Podell E., Zhou K., Golden B.L., Szewczak A.A., Kundrot C.E., CechT.R., Doudna J.A. (1996). RNA tertiary structure mediation by adenosine platforms. Science 273: 1696-1699
Chang G. & Lewis M. (1994), Acta Cryst. D50, 667-674.
Chang G. & Lewis M. (1997) Molecular Replacement Using Genetic Algorithms. Acta Cryst. D53, 279-289.
Crowther R.A. & Blow D.M. (1967), Acta Cryst. 23, 544-548.
Crowther R.A. (1972) in “The Molecular Replacement Method”, Int. Sci. Rev. No.13 (Rossmann M.G., ed.). Gordon & Breach, New York.
Draper D.E. (1995). Protein-RNA recognition. Annu. Rev. Biochem. 64: 593-620
Draper D.E. (1996) Ribosomal protein-RNA interactions. In Ribosomal RNA: structure, evolution, processing and function in protein biosynthesis. Eds. Zimmermann R.A., Dahlberg A.E. Boca Raton, Florida, CRC Press, 171-198
Franklin C., Shi J.P., Shimmel P. (1992). Overlapping nucleotide determinante for specific aminocylation of RNA. Science. 225: 1121-1125
Fujinaga M. & Read R.J. (1987), J. Appl. Cryst. 20, 517-521.
Harada Y., Lifchitz A., Berthou J., Jolles P. (1981), Acta Cryst. A37, 398-406.
Huber R. (1965), Acta Cryst. A19, 353-356.
Kjems J., Egebjerg J., Christiansen J. (1998) Laboratory techniques in biochemistry and molecular biology. Elsevier, 237
Kim J.L., Nikolov D.B., Burley S.K. (1993). Co-crystal structure of TBP recognizing the minor groove of a TATA element. Nature 365: 520-527
Kirkpatrick S., Gelatt C.D. Jr & Vecchi M.P. (1983), Science, 220, 671-680.
Kissinger C.R., Gehlhaar D.K., Fogel D.B. (1999) Rapid automated molecular replacement by evolutionary search. Acta Cryst. D55, 484-491.
Marino J.P., Gregorian R.S., Csankovski G., Grothers D.M. (1995). Ent helix formation between RNA hairpins with complementary loops. Science 268: 1448-1254
Metropolis N., Rosenbluth A.W., Rosenbluth M.N., Teller A. & Teller E. (1953), J. Chem. Phys. 21, 1087-1092.
Miller S.T., Hogle J.M. & Filman D.J. (1996), Acta Cryst. D52, 235-251.
Musco G., stier G., Joseph C., Morelli M.A.C., Nilges M., Gibson T.J., Pastore A.. (1996) Thre-dimensional structure and stability of the KH domain: molecular insight into the fragile X syndrome. Cell 85: 237-245
Nevskaya, N., Tishchenko, S., Nikulin, A., Al-Karadaghi, S., Liljas, A., Ehresmann, B., Ehresmann, C., Garber, M., Nikonov, S. (1998) Crystal Structure of Ribosomal Protein S8 from Thermus Thermophilus Reveals a High Degree of Structural Conservation of a Specific RNA Binding Site. J.Mol.Biol. 279, 233-244.
Normanly J., Abelson J. (1989). TRNA identity. Annu. Rev. Biochem. 58: 1029-1049
Powell M.J.D. (1977), Math. Programming, 12, 241-254.
Read R.J. (1997) Model Phases: Probabilities and Bias. In Methods in Enzymology, 277, 110-128, Academic Press.
Read R.J. & Schierbeek A.J. (1988), J. Appl. Cryst. 21, 490-495.
Rossmann M.G., Blow D.M., Harding M.M., Coller E. (1964), Acta Cryst. 17, 338-342.
Rossmann M.G. & Blow D.M. (1962), Acta Cryst. 15, 24-31
Schindelin H., Marahiel M.A., Heinemann U. (1993). Universal nucleic acid-binding domain revealed by crystal structure og the B.subtilis major cold-shock domain. Nature 364: 164-168
Seeman N., Rosenberg J.M., Rich A. (1976). Sequence-specific recgnition of double helical nucleic acids by proteins. Pros. Natl, Acad. USA 73: 804-808
von Hippel P.H., McGhee J.D. (1972). DNA-protein interactions. Annu. Rev. Biochem. 41: 231-298
Weeks K.M., Crothers D.M. (1993). Major grove accessibility of RNA. Science 261: 1574-1577
Дата: 2019-07-24, просмотров: 269.